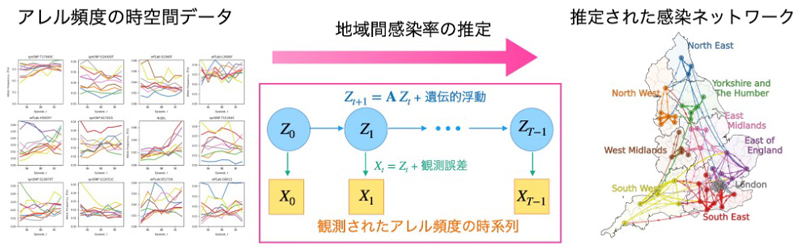
COVID-19のパンデミックは、病原体がどのように地域を越えて広がっていくのかという「地域間伝播」の重要性を再認識させました。従来は、人の移動データや接触履歴に基づいて伝播を推定してきましたが、社会的・地理的に離れた地域間で起きるような稀な伝播イベントを捉えることは困難でした。
岡田崇 医生物学研究所准教授、Giulio Isacchini 米国カリフォルニア大学バークレー校(University of California, Berkeley)研究員、QinQin Yu 米国ハーバード大学(Harvard University)研究員、Oskar Hallatschek 米国カリフォルニア大学バークレー校教授の研究グループは、SARS-CoV-2の豊富なゲノムデータに着目し、各地域のアレル頻度の時系列データから感染伝播の流入を直接推定する数理手法を開発しました。観測誤差やアレル頻度の揺らぎも考慮するために隠れマルコフモデルを利用しています。この手法を英国および米国のSARS-CoV-2データに適用した結果、変異株ごとに地域間の感染ネットワークがどのように変化するかに加えて、感染伝播がどの程度の時間スケールで起きているか、また、その速度が地域間でどのように異なるかといった動態も明らかになりました。本研究は、ゲノムデータに基づく新たな時系列解析の道を拓くものであり、今後の疫学モニタリングや病原体の拡散予測モデルへの応用だけでなく、さまざまなゲノムデータへの応用が期待されます。
本研究成果は、2025年11月26日に、国際学術誌「PNAS(米国科学アカデミー紀要)」にオンライン掲載されました。
【DOI】
https://doi.org/10.1073/pnas.2500663122
【KURENAIアクセスURL】
http://hdl.handle.net/2433/298377
【書誌情報】
Takashi Okada, Giulio Isacchini, QinQin Yu, Oskar Hallatschek (2025). Uncovering heterogeneous intercommunity disease transmission from neutral allele frequency time series. Proceedings of the National Academy of Sciences (PNAS), 122, 48, e2500663122.